Laboratorio de Biología y Química Vegetal - Genética y Genómica de Vid
De Mendoza CONICET
(→Líneas de Investigación) |
(→Publicaciones) |
||
| (184 ediciones intermedias no se muestran.) | |||
| Línea 1: | Línea 1: | ||
| - | + | '''''[[Grapevine Genetic and Genomic Group (*English*)]]''''' [[Archivo:English Xsmall.gif|rigth]] | |
| + | ---- | ||
| + | = '''GRUPO DE GENÉTICA Y GENÓMICA DE VID'''= | ||
| + | |||
| + | |||
=== Líneas de Investigación === | === Líneas de Investigación === | ||
[[Imagen:Lineas small.png|right]] | [[Imagen:Lineas small.png|right]] | ||
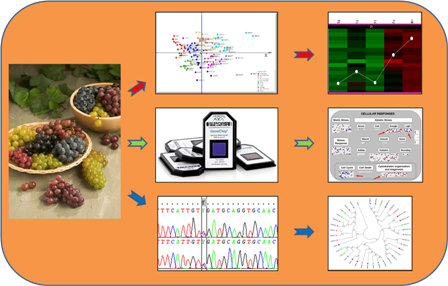
| - | Nuestro grupo de investigación está interesado en conocer los mecanismos genéticos y moleculares responsables de la regulación de diferentes caracteres relacionados con la calidad de | + | Nuestro grupo de investigación está interesado en conocer los mecanismos genéticos y moleculares de la vid, responsables de la regulación de diferentes caracteres relacionados con la calidad de las uvas y el vino. En particular nuestra actividad se centra en el estudio del control genético de los perfiles de antocianos en la piel de las uvas, el análisis genético y molecular de la familia génica estilbeno sintasa (STS) que regula la producción de resveratrol y el estudio de genes que intervienen en determinación del tamaño y la forma de la baya. |
| - | Nuestra aproximación se basa en caracterizar y explotar la variación genética natural que existe en la vid para estos caracteres utilizando herramientas genéticas y genómicas. Para ello, colaboramos con otros grupos en la caracterización de | + | Nuestra aproximación se basa en caracterizar y explotar la variación genética natural que existe en la vid para estos caracteres utilizando herramientas genéticas y genómicas. Para ello, colaboramos también con otros grupos en la caracterización y análisis genético de distintos materiales de vid (variedades, accesiones silvestres, clones, variantes somáticas y poblaciones de mapeo). Además, participamos en el desarrollo y aplicación de nuevas herramientas de análisis genómico como marcadores moleculares de tipo SNP y micro-satélites, así como microarrays de vid para el análisis de expresión génica global (transcriptómica). |
El conocimiento generado tiene aplicación directa en la selección de clones y variedades con nuevas características productivas. Por otra parte, las herramientas obtenidas tienen una amplia aplicación en la identificación varietal o en el seguimiento del desarrollo de la vid o de su respuesta a distintas condiciones ambientales o de cultivo. | El conocimiento generado tiene aplicación directa en la selección de clones y variedades con nuevas características productivas. Por otra parte, las herramientas obtenidas tienen una amplia aplicación en la identificación varietal o en el seguimiento del desarrollo de la vid o de su respuesta a distintas condiciones ambientales o de cultivo. | ||
| Línea 15: | Línea 19: | ||
=== Integrantes === | === Integrantes === | ||
| - | *''' | + | *'''Diego Lijavetzky''' - Investigador Adjunto (CONICET) (Jefe de Grupo) [[Media:CV_Abr2014.pdf]] |
| - | *'''Claudio Muñoz''' - Becario Posgrado Tipo | + | *'''Claudio Muñoz''' - Becario Posgrado Tipo II (CONICET) |
| - | *'''Constanza Soledad Chialva''' - Becaria Posgrado Tipo I (CONICET) | + | *'''Constanza Soledad Chialva''' - Becaria Posgrado Tipo II (CONICET) |
| - | *''' | + | *'''Estefanía Eichler''' - Becaria Posgrado Tipo I (CONICET) |
| - | [[Archivo: | + | *'''Silvina Van Houten''' - Becaria Pregrado - Beca Estímulo (CIN) |
| + | [[Archivo:Foto_grupo_2014_small.jpg]] | ||
| + | |||
| + | === Colaboraciones === | ||
| + | *INTA Mendoza (Sebastian Gomez Talquenca, Mariana Combina, Martín Fanzone) | ||
| + | *Universidad de Chile (Álvaro Peña) | ||
| + | *INIA La Platina-Chile (Humberto Prieto) | ||
| + | *Instituto de la Ciencia de la Vid y el Vino-Logroño, España (José Miguel Martinez Zapater, Javier Ibañez, Pablo Carbonell Bejerano) | ||
---- | ---- | ||
=== Publicaciones === | === Publicaciones === | ||
| - | * Martínez-Esteso MJ, Sellés-Marchart S, LIJAVETZKY D, Pedreño MA and Bru-Martínez R: '''A DIGE-based quantitative proteomic analysis of grape berry flesh development and ripening reveals key events in sugar and organic acid metabolism'''. '' | + | 2014 |
| - | * Pontin MA, Piccoli PN, Francisco R, Bottini R, Martinez-Zapater JM and LIJAVETZKY D:''' Transcriptome changes in grapevine (''Vitis vinifera'' L.) cv. Malbec leaves induced by ultraviolet-B radiation'''. ''BMC Plant | + | *Almagro L, Carbonell-Bejerano P, Belchí-Navarro S, Bru R, Martinez-Zapater JM, LIJAVETZKY D, Pedreño MA. 2014. '''Dissecting the transcriptional response to elicitors in Vitis vinifera cells'''. PLoS ONE. In press. |
| - | * Martinez-Zapater JM, Carmona MJ, Díaz-Riquelme J, Fernández L and LIJAVETZKY D: '''Grapevine Genetics after the Genome Sequence: Challenges and Limitations'''. '' | + | *MUÑOZ CJ, Gomez-Talquenca S, CHIALVA C, Ibáñez J, Martinez-Zapater JM, Pena-Neira A, LIJAVETZKY D. 2014. '''Relationships among gene expression and anthocyanin composition of Malbec grapevine clones'''. ''Journal of Agricultural and Food Chemistry,62, 6716-6725'' . |
| - | * Diaz-Riquelme J#, LIJAVETZKY , D#, Martinez-Zapater JM, Carmona MJ: '''Genome-Wide Analysis of MIKCC-Type MADS-Box Genes in Grapevine'''. ''Plant | + | 2013 |
| + | * Carbonell-Bejerano, P, Santa Maria, E, Torres-Perez, R, Royo, C, LIJAVETZKY, D, Bravo, G, Aguirreolea, J, Sanchez-Diaz, M, Antolin, MC and Martinez-Zapater, JM. 2013: '''Thermotolerance Responses in Ripening Berries of Vitis vinifera L. cv Muscat Hamburg'''. ''Plant Cell Physiol. 54, 1200-1216''. | ||
| + | 2012 | ||
| + | * LIJAVETZKY D, Carbonell Bejerano P, Grimplet P, Bravo G, Flores P, Fenoll J, Hellín P, Oliveros JC, Martínez Zapater JM. 2012: '''Berry Flesh and Skin Ripening Features in ''Vitis vinifera'' as Assessed by Transcriptional Profiling'''. PLoS ONE 7(6): e39547. doi:10.1371/journal.pone.0039547 | ||
| + | * Belchí-Navarro S, Almagro L, LIJAVETZKY D, Bru R and Pedreño MA. 2012: '''Enhanced extracellular production of trans-resveratrol in ''Vitis vinifera'' suspension cultured cells by using cyclodextrins and methyljasmonate'''. ''Plant Cell Reports 31, 81-89''. | ||
| + | 2011 | ||
| + | * Cabezas J, Ibanez J, LIJAVETZKY D, Velez D, Bravo G, Rodriguez V, Carreno I, Jermakow A, Carreno J, Ruiz-Garcia L, Thomas M, Martinez-Zapater J. 2011: '''A 48 SNP Set for Grapevine Cultivar Identification'''. ''BMC Plant Biology 11, 153''. | ||
| + | * Martínez-Esteso MJ, Sellés-Marchart S, LIJAVETZKY D, Pedreño MA and Bru-Martínez R: '''A DIGE-based quantitative proteomic analysis of grape berry flesh development and ripening reveals key events in sugar and organic acid metabolism'''. ''Journal of Experimental Botany 2011, 62, 2521-2569''.¶ | ||
| + | *Nally M, Pesce V, Maturano Y, MUÑOZ C, Combina M, Toro M, de Figueroa L, Vazquez F: 2012. '''Biocontrol of ''Botrytis cinerea'' in table grapes by non-pathogenic indigenous ''Saccharomyces cerevisiae'' yeasts isolated from viticultural environments in Argentina'''. ''Postharvest Biology and Technology 64, 40-48''. | ||
| + | 2010 | ||
| + | * Pontin MA, Piccoli PN, Francisco R, Bottini R, Martinez-Zapater JM and LIJAVETZKY D:''' Transcriptome changes in grapevine (''Vitis vinifera'' L.) cv. Malbec leaves induced by ultraviolet-B radiation'''. ''BMC Plant Biology 2010, 10:224''. | ||
| + | * Martinez-Zapater JM, Carmona MJ, Díaz-Riquelme J, Fernández L and LIJAVETZKY D: '''Grapevine Genetics after the Genome Sequence: Challenges and Limitations'''. ''Australian Journal of Grape Wine Research 2010, 16(s1):33-46''. | ||
| + | * MUÑOZ C, Gómez Talquenca S, Oriolani E, Combina M. '''Genetic characterization of grapevine-infecting Botrytis cinerea isolates from Argentina'''. ''Revista Iberoamericana de Micología 2010, 27:66-70''. | ||
| + | 2009 | ||
| + | * Gómez Talquenca S, MUÑOZ C, Grau O, Gracia O. '''First description of Grapevine leafroll-associated virus 5 in Argentina and partial genome sequence'''. ''Virus Genes 2009, 38:184-186''. | ||
| + | * Diaz-Riquelme J#, LIJAVETZKY , D#, Martinez-Zapater JM, Carmona MJ: '''Genome-Wide Analysis of MIKCC-Type MADS-Box Genes in Grapevine'''. ''Plant Physiology 2009, 149:354-369''. #Equal contributors. | ||
| + | * MUÑOZ C, Gómez Talquenca S, Volpe ML. '''Tetra primer ARMS-PCR for identification of SNP in [beta]-tubulin of Botrytis cinerea, responsible of resistance to benzimidazole'''. ''Journal of Microbiological Methods 2009, 78:245-246''. | ||
| + | 2008 | ||
* LIJAVETZKY D#, Almagro L#, Belchi-Navarro S, Martinez-Zapater JM, Bru R, Pedreno MA: '''Synergistic effect of methyljasmonate and cyclodextrin on stilbene biosynthesis pathway gene expression and resveratrol production in Monastrell grapevine cell cultures'''. ''BMC Research Notes 2008, 1:132''. #Equal contributors | * LIJAVETZKY D#, Almagro L#, Belchi-Navarro S, Martinez-Zapater JM, Bru R, Pedreno MA: '''Synergistic effect of methyljasmonate and cyclodextrin on stilbene biosynthesis pathway gene expression and resveratrol production in Monastrell grapevine cell cultures'''. ''BMC Research Notes 2008, 1:132''. #Equal contributors | ||
| + | 2007 | ||
* LIJAVETZKY D, Cabezas JA, Ibanez A, Rodriguez V, Martinez-Zapater JM: '''High throughput SNP discovery and genotyping in grapevine (''Vitis vinifera ''L.) by combining a re-sequencing approach and SNPlex technology'''. ''BMC Genomics 2007, 8:424''. | * LIJAVETZKY D, Cabezas JA, Ibanez A, Rodriguez V, Martinez-Zapater JM: '''High throughput SNP discovery and genotyping in grapevine (''Vitis vinifera ''L.) by combining a re-sequencing approach and SNPlex technology'''. ''BMC Genomics 2007, 8:424''. | ||
* Peng FY, Reid KE, Liao N, Schlosser J, LIJAVETZKY D, Holt R, Martinez-Zapater JM, Jones S, Marra M, Bohlmann J, Lund ST: '''Generation of ESTs in ''Vitis vinifera'' wine grape (Cabernet Sauvignon) and table grape (Muscat Hamburg) and discovery of new candidate genes with possible roles in berry development'''. ''Gene 2007, 402:40-50''. | * Peng FY, Reid KE, Liao N, Schlosser J, LIJAVETZKY D, Holt R, Martinez-Zapater JM, Jones S, Marra M, Bohlmann J, Lund ST: '''Generation of ESTs in ''Vitis vinifera'' wine grape (Cabernet Sauvignon) and table grape (Muscat Hamburg) and discovery of new candidate genes with possible roles in berry development'''. ''Gene 2007, 402:40-50''. | ||
| + | 2006 | ||
* LIJAVETZKY D, Ruiz-Garcia L, Cabezas JA, De Andres MT, Bravo G, Ibanez A, Carreno J, Cabello F, Ibanez J, Martinez-Zapater JM: '''Molecular genetics of berry colour variation in table grape'''. ''Mol Genet Genomics 2006, 276:427-435''. | * LIJAVETZKY D, Ruiz-Garcia L, Cabezas JA, De Andres MT, Bravo G, Ibanez A, Carreno J, Cabello F, Ibanez J, Martinez-Zapater JM: '''Molecular genetics of berry colour variation in table grape'''. ''Mol Genet Genomics 2006, 276:427-435''. | ||
| + | <2005 | ||
* LIJAVETZKY D, Carbonero P, Vicente-Carbajosa J: '''Genome-wide comparative phylogenetic analysis of the rice and Arabidopsis Dof gene families'''. ''BMC Evolutionary Biology 2003, 3''. | * LIJAVETZKY D, Carbonero P, Vicente-Carbajosa J: '''Genome-wide comparative phylogenetic analysis of the rice and Arabidopsis Dof gene families'''. ''BMC Evolutionary Biology 2003, 3''. | ||
* Helguera M, Khan IA, Kolmer J, LIJAVETZKY D, Zhong-qi L, Dubcovsky J: '''PCR assays for the Lr37-Yr17-Sr38 cluster of rust resistance genes and their use to develop isogenic hard red spring wheat lines'''. ''Crop Science 2003, 43:1839-1847''. | * Helguera M, Khan IA, Kolmer J, LIJAVETZKY D, Zhong-qi L, Dubcovsky J: '''PCR assays for the Lr37-Yr17-Sr38 cluster of rust resistance genes and their use to develop isogenic hard red spring wheat lines'''. ''Crop Science 2003, 43:1839-1847''. | ||
| Línea 45: | Línea 76: | ||
=== Proyectos financiados === | === Proyectos financiados === | ||
| - | * ''' | + | * '''Genética y genómica de la vid aplicada al estudio de caracteres de calidad de la uva'''. 06/A587. Proyectos Bienales 2013-2015. SeCTyP-UNCUYO. (IP: Diego Lijavetzky) |
| - | * '''Caracterización de | + | * '''Caracterización del efecto de GLRaV-2 sobre parámetros fisiológicos del cv. Malbec, y su impacto en lacalidad de la producción'''. PICT-2012-0396. Agencia Nacional de Promoción Científica y Tecnológica. (IP: Sebastián Gómez Talquenca) |
| - | + | * '''An integrated systems approach to determine the developmental mechanisms controlling fleshy fruit quality in tomato and grapevine'''. COST Action FA1106 (QUALITYFRUIT). European Union Framework Programme. (MC Chair: Prof. Mondher Bouzayen; Vice-Chair: Prof. Mario Pezzotti) | |
| - | * ''' | + | * '''Plant Metabolic Engineering for High Value Products'''. COST ACTION FA1006. European Union Framework Programme. (MC Chair: Prof. Heribert Warzecha) |
| - | * ''' | + | |
| - | + | ---- | |
| - | + | ||
| + | === Difusión === | ||
| + | [[Archivo:Radio_small.jpg]] ==> '''''[http://youtu.be/2YSWrvY6DwI ENTREVISTA SOBRE RESVERATROL en RADIO DEL PLATA (Cristina Pérez)]'''''< == | ||
| + | [[Archivo:Radio2_small.jpg]] | ||
| + | |||
| + | |||
| + | |||
| Línea 58: | Línea 95: | ||
|<p style="text-align:center; font-size: 140%; line-height: 95%"> | |<p style="text-align:center; font-size: 140%; line-height: 95%"> | ||
| - | + | == Contacto == | |
| - | Instituto de Biología Agrícola de Mendoza (IBAM) | + | Instituto de Biología Agrícola de Mendoza (IBAM-CONICET) |
Facultad de Ciencias Agrarias-UNCuyo | Facultad de Ciencias Agrarias-UNCuyo | ||
| Línea 74: | Línea 111: | ||
E-mail2: [mailto:diegolija@hotmail.com diegolija@hotmail.com] | E-mail2: [mailto:diegolija@hotmail.com diegolija@hotmail.com] | ||
| + | |||
| + | Web: [http://bit.ly/IBAM-Genetica_y_Genomica_de_Vid http://bit.ly/IBAM-Genetica_y_Genomica_de_Vid] | ||
---- | ---- | ||
última version al 10:33 8 oct 2014
Grapevine Genetic and Genomic Group (*English*) ![]()
Contenido |
GRUPO DE GENÉTICA Y GENÓMICA DE VID
Líneas de Investigación
Nuestro grupo de investigación está interesado en conocer los mecanismos genéticos y moleculares de la vid, responsables de la regulación de diferentes caracteres relacionados con la calidad de las uvas y el vino. En particular nuestra actividad se centra en el estudio del control genético de los perfiles de antocianos en la piel de las uvas, el análisis genético y molecular de la familia génica estilbeno sintasa (STS) que regula la producción de resveratrol y el estudio de genes que intervienen en determinación del tamaño y la forma de la baya.
Nuestra aproximación se basa en caracterizar y explotar la variación genética natural que existe en la vid para estos caracteres utilizando herramientas genéticas y genómicas. Para ello, colaboramos también con otros grupos en la caracterización y análisis genético de distintos materiales de vid (variedades, accesiones silvestres, clones, variantes somáticas y poblaciones de mapeo). Además, participamos en el desarrollo y aplicación de nuevas herramientas de análisis genómico como marcadores moleculares de tipo SNP y micro-satélites, así como microarrays de vid para el análisis de expresión génica global (transcriptómica).
El conocimiento generado tiene aplicación directa en la selección de clones y variedades con nuevas características productivas. Por otra parte, las herramientas obtenidas tienen una amplia aplicación en la identificación varietal o en el seguimiento del desarrollo de la vid o de su respuesta a distintas condiciones ambientales o de cultivo.
Integrantes
- Diego Lijavetzky - Investigador Adjunto (CONICET) (Jefe de Grupo) Media:CV_Abr2014.pdf
- Claudio Muñoz - Becario Posgrado Tipo II (CONICET)
- Constanza Soledad Chialva - Becaria Posgrado Tipo II (CONICET)
- Estefanía Eichler - Becaria Posgrado Tipo I (CONICET)
- Silvina Van Houten - Becaria Pregrado - Beca Estímulo (CIN)
Colaboraciones
- INTA Mendoza (Sebastian Gomez Talquenca, Mariana Combina, Martín Fanzone)
- Universidad de Chile (Álvaro Peña)
- INIA La Platina-Chile (Humberto Prieto)
- Instituto de la Ciencia de la Vid y el Vino-Logroño, España (José Miguel Martinez Zapater, Javier Ibañez, Pablo Carbonell Bejerano)
Publicaciones
2014
- Almagro L, Carbonell-Bejerano P, Belchí-Navarro S, Bru R, Martinez-Zapater JM, LIJAVETZKY D, Pedreño MA. 2014. Dissecting the transcriptional response to elicitors in Vitis vinifera cells. PLoS ONE. In press.
- MUÑOZ CJ, Gomez-Talquenca S, CHIALVA C, Ibáñez J, Martinez-Zapater JM, Pena-Neira A, LIJAVETZKY D. 2014. Relationships among gene expression and anthocyanin composition of Malbec grapevine clones. Journal of Agricultural and Food Chemistry,62, 6716-6725 .
2013
- Carbonell-Bejerano, P, Santa Maria, E, Torres-Perez, R, Royo, C, LIJAVETZKY, D, Bravo, G, Aguirreolea, J, Sanchez-Diaz, M, Antolin, MC and Martinez-Zapater, JM. 2013: Thermotolerance Responses in Ripening Berries of Vitis vinifera L. cv Muscat Hamburg. Plant Cell Physiol. 54, 1200-1216.
2012
- LIJAVETZKY D, Carbonell Bejerano P, Grimplet P, Bravo G, Flores P, Fenoll J, Hellín P, Oliveros JC, Martínez Zapater JM. 2012: Berry Flesh and Skin Ripening Features in Vitis vinifera as Assessed by Transcriptional Profiling. PLoS ONE 7(6): e39547. doi:10.1371/journal.pone.0039547
- Belchí-Navarro S, Almagro L, LIJAVETZKY D, Bru R and Pedreño MA. 2012: Enhanced extracellular production of trans-resveratrol in Vitis vinifera suspension cultured cells by using cyclodextrins and methyljasmonate. Plant Cell Reports 31, 81-89.
2011
- Cabezas J, Ibanez J, LIJAVETZKY D, Velez D, Bravo G, Rodriguez V, Carreno I, Jermakow A, Carreno J, Ruiz-Garcia L, Thomas M, Martinez-Zapater J. 2011: A 48 SNP Set for Grapevine Cultivar Identification. BMC Plant Biology 11, 153.
- Martínez-Esteso MJ, Sellés-Marchart S, LIJAVETZKY D, Pedreño MA and Bru-Martínez R: A DIGE-based quantitative proteomic analysis of grape berry flesh development and ripening reveals key events in sugar and organic acid metabolism. Journal of Experimental Botany 2011, 62, 2521-2569.¶
- Nally M, Pesce V, Maturano Y, MUÑOZ C, Combina M, Toro M, de Figueroa L, Vazquez F: 2012. Biocontrol of Botrytis cinerea in table grapes by non-pathogenic indigenous Saccharomyces cerevisiae yeasts isolated from viticultural environments in Argentina. Postharvest Biology and Technology 64, 40-48.
2010
- Pontin MA, Piccoli PN, Francisco R, Bottini R, Martinez-Zapater JM and LIJAVETZKY D: Transcriptome changes in grapevine (Vitis vinifera L.) cv. Malbec leaves induced by ultraviolet-B radiation. BMC Plant Biology 2010, 10:224.
- Martinez-Zapater JM, Carmona MJ, Díaz-Riquelme J, Fernández L and LIJAVETZKY D: Grapevine Genetics after the Genome Sequence: Challenges and Limitations. Australian Journal of Grape Wine Research 2010, 16(s1):33-46.
- MUÑOZ C, Gómez Talquenca S, Oriolani E, Combina M. Genetic characterization of grapevine-infecting Botrytis cinerea isolates from Argentina. Revista Iberoamericana de Micología 2010, 27:66-70.
2009
- Gómez Talquenca S, MUÑOZ C, Grau O, Gracia O. First description of Grapevine leafroll-associated virus 5 in Argentina and partial genome sequence. Virus Genes 2009, 38:184-186.
- Diaz-Riquelme J#, LIJAVETZKY , D#, Martinez-Zapater JM, Carmona MJ: Genome-Wide Analysis of MIKCC-Type MADS-Box Genes in Grapevine. Plant Physiology 2009, 149:354-369. #Equal contributors.
- MUÑOZ C, Gómez Talquenca S, Volpe ML. Tetra primer ARMS-PCR for identification of SNP in [beta]-tubulin of Botrytis cinerea, responsible of resistance to benzimidazole. Journal of Microbiological Methods 2009, 78:245-246.
2008
- LIJAVETZKY D#, Almagro L#, Belchi-Navarro S, Martinez-Zapater JM, Bru R, Pedreno MA: Synergistic effect of methyljasmonate and cyclodextrin on stilbene biosynthesis pathway gene expression and resveratrol production in Monastrell grapevine cell cultures. BMC Research Notes 2008, 1:132. #Equal contributors
2007
- LIJAVETZKY D, Cabezas JA, Ibanez A, Rodriguez V, Martinez-Zapater JM: High throughput SNP discovery and genotyping in grapevine (Vitis vinifera L.) by combining a re-sequencing approach and SNPlex technology. BMC Genomics 2007, 8:424.
- Peng FY, Reid KE, Liao N, Schlosser J, LIJAVETZKY D, Holt R, Martinez-Zapater JM, Jones S, Marra M, Bohlmann J, Lund ST: Generation of ESTs in Vitis vinifera wine grape (Cabernet Sauvignon) and table grape (Muscat Hamburg) and discovery of new candidate genes with possible roles in berry development. Gene 2007, 402:40-50.
2006
- LIJAVETZKY D, Ruiz-Garcia L, Cabezas JA, De Andres MT, Bravo G, Ibanez A, Carreno J, Cabello F, Ibanez J, Martinez-Zapater JM: Molecular genetics of berry colour variation in table grape. Mol Genet Genomics 2006, 276:427-435.
<2005
- LIJAVETZKY D, Carbonero P, Vicente-Carbajosa J: Genome-wide comparative phylogenetic analysis of the rice and Arabidopsis Dof gene families. BMC Evolutionary Biology 2003, 3.
- Helguera M, Khan IA, Kolmer J, LIJAVETZKY D, Zhong-qi L, Dubcovsky J: PCR assays for the Lr37-Yr17-Sr38 cluster of rust resistance genes and their use to develop isogenic hard red spring wheat lines. Crop Science 2003, 43:1839-1847.
- Carrari F, Benech-Arnold R, Osuna-Fernandez R, Hopp E, Sanchez R, Iusem N, LIJAVETZKY D: Genetic mapping of the Sorghum bicolor vp1 gene and its relationship with pre-harvest sprouting resistance. Genome 2003, 46:253-258.
- Carrari F, Perez-Flores L, LIJAVETZKY D, Enciso S, Sanchez R, Benech-Arnold R, Iusem N: Cloning and expression of a sorghum gene with homology to maize vp1. Its potential involvement in pre-harvest sprouting resistance. Plant Molecular Biology 2001, 45:631-640.
- Carrari F, Frankel N, LIJAVETZKY D, Benech-Arnold R, Sanchez R, Iusem ND: The Tata-less promoter of VP1, a plant gene controlling seed germination. DNA Sequence 2001, 12:107-114.
- LIJAVETZKY D, Martinez MC, Carrari F, Hopp HE: QTL analysis and mapping of pre-harvest sprouting resistance in sorghum. Euphytica 2000, 112:125-135.
- Tranquilli G, LIJAVETZKY D, Muzzi G, Dubcovsky J: Genetic and physical characterization of grain texture-related loci in diploid wheat. Molecular and General Genetics 1999, 262:846-850.
- LIJAVETZKY D, Muzzi G, Wicker T, Keller B, Wing R, Dubcovsky J: Construction and characterization of a bacterial artificial chromosome (BAC) library for the A genome of wheat. Genome 1999, 42:1176-1182.
- Dubcovsky J, LIJAVETZKY D, Appendino L, Tranquilli G: Comparative RFLP mapping of Triticum monococcum genes controlling vernalization requirement. Theoretical and Applied Genetics 1998, 97:968-975.
- Rossi M, LIJAVETZKY D, Bernacchi D, Hopp HE, Iusem N: Asr genes belong to a gene family comprising at least three closely linked loci on chromosome 4 in tomato. Molecular & General Genetics 1996, 252:489-492.
Proyectos financiados
- Genética y genómica de la vid aplicada al estudio de caracteres de calidad de la uva. 06/A587. Proyectos Bienales 2013-2015. SeCTyP-UNCUYO. (IP: Diego Lijavetzky)
- Caracterización del efecto de GLRaV-2 sobre parámetros fisiológicos del cv. Malbec, y su impacto en lacalidad de la producción. PICT-2012-0396. Agencia Nacional de Promoción Científica y Tecnológica. (IP: Sebastián Gómez Talquenca)
- An integrated systems approach to determine the developmental mechanisms controlling fleshy fruit quality in tomato and grapevine. COST Action FA1106 (QUALITYFRUIT). European Union Framework Programme. (MC Chair: Prof. Mondher Bouzayen; Vice-Chair: Prof. Mario Pezzotti)
- Plant Metabolic Engineering for High Value Products. COST ACTION FA1006. European Union Framework Programme. (MC Chair: Prof. Heribert Warzecha)
Difusión
 ==> ENTREVISTA SOBRE RESVERATROL en RADIO DEL PLATA (Cristina Pérez)< ==
==> ENTREVISTA SOBRE RESVERATROL en RADIO DEL PLATA (Cristina Pérez)< ==

ContactoInstituto de Biología Agrícola de Mendoza (IBAM-CONICET) Facultad de Ciencias Agrarias-UNCuyo Almirante Brown 500 - (5505) Chacras de Coria, Mendoza, Argentina Tel: +54 261 4135010 Ext. 1307 FAX: +54 261 4960469 E-mail1: dlijavetzky@conicet.gov.ar E-mail2: diegolija@hotmail.com Web: http://bit.ly/IBAM-Genetica_y_Genomica_de_Vid Mayor información: ver página personal |